Secuenciación del SARS-CoV-2: la iniciativa tecnológica para fortalecer los sistemas de alerta temprana ante emergencias de salud pública en Latinoamérica y el Caribe
Resumen
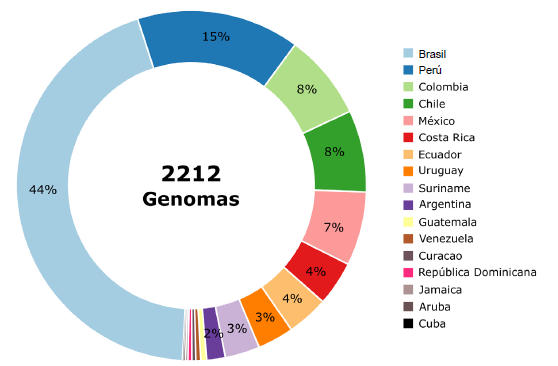
La pandemia de COVID-19 causada por el SARS-CoV-2 es un problema de salud pública sin precedentes en los últimos 100 años, así como la respuesta centrada en la caracterización genómica del SARS-CoV-2 prácticamente en todas las regiones del planeta. Esta pandemia surgió durante la era de la epidemiología genómica impulsada por los continuos avances en la secuenciación de próxima generación. Desde su reciente aparición, la epidemiología genómica permitió la identificación precisa de nuevos linajes o especies de agentes patógenos y la reconstrucción de su variabilidad genética en tiempo real, lo que se hizo evidente en los brotes de influenza H1N1, MERS y SARS. Sin embargo, la escala global y descontrolada de esta pandemia ha generado una situación que obligó a utilizar de forma masiva herramientas de la epidemiología genómica como la rápida identificación del SARS-CoV-2 y el registro de nuevos linajes y su vigilancia activa en todo el mundo. Antes de la pandemia de COVID-19 la disponibilidad e datos genómicos de agentes patógenos circulantes en varios países de Latinoamérica y el Caribe era escasa o nula. Con la llegada del SARS-CoV-2 dicha situación cambió significativamente, aunque la cantidad de información disponible sigue siendo escasa y, en países como Colombia, Brasil, Argentina y Chile, la información genómica del SARS-CoV-2 provino principalmente de grupos de investigación en epidemiología genómica más que como producto de una política o programa de vigilancia en salud pública.
Descargas
Referencias bibliográficas
Dong E, Du H, Gardner L. An interactive web-based dashboard to track COVID-19 in real time. Lancet Infect Dis. 2020;20:533-4. https://doi.org/10.1016/S1473-3099(20)30120-1
World Health Organization-WHO. Rolling updates on coronavirus disease (COVID-19). Geneva: World Health Organization; 2020. Fecha de consulta: 31 de julio de 2020.
Disponible en: https://www.who.int/emergencies/diseases/novel-coronavirus-2019/events-asthey-happen
Miller MJ, Loaiza JR, Takyar A, Gilman RH. COVID-19 in Latin America: Novel transmission dynamics for a global pandemic? PLoS Negl Trop Dis. 2020;14:e0008265. https://doi.org/10.1371/journal.pntd.0008265
United Nations. The impact of COVID-19 on Latin America and the Caribbean. New York: United Nations; 2020. p. 25.
Anderson RM, Heesterbeek H, Klinkenberg D, Hollingsworth TD. How will country-based mitigation measures influence the course of the COVID-19 epidemic? Lancet. 2020;395:931-4. https://doi.org/10.1016/S0140-6736(20)30567-5
Guthrie JL, Gardy JL. A brief primer on genomic epidemiology: Lessons learned from Mycobacterium tuberculosis. Ann N Y Acad Sci. 2017;1388:59-77. https://doi.org/10.1111/nyas.13273
Zhu N, Zhang D, Wang W, Li X, Yang B, Song J, et al. A novel coronavirus from patients with pneumonia in China, 2019. N Engl J Med. 2020;382:727-33. https://doi.org/10.1056/NEJMoa2001017
Quick J. nCoV-2019 sequencing protocol: protocols.io; 2020. Fecha de consulta: 2 de marzo de 2020. Disponible en: https://www.protocols.io/view/ncov-2019-sequencing-protocol-bbmuik6w
Álvarez-Díaz DA, Franco-Muñoz C, Laiton-Donato K, Usme-Ciro JA, Franco-Sierra ND, Flórez-Sánchez AC, et al. Molecular analysis of several in-house rRT-PCR protocols for SARS-CoV-2 detection in the context of genetic variability of the virus in Colombia. Infect Genet Evol. 2020;84:104390. https://doi.org/10.1016/j.meegid.2020.104390
Franco-Muñoz C, Álvarez-Díaz DA, Laiton-Donato K, Wiesner M, Escandón P, Usme-Ciro JA, et al. Substitutions in spike and nucleocapsid proteins of SARS-CoV-2 circulating in South America. Infect Genet Evol. 2020;85:104557. https://doi.org/10.1016/j.meegid.2020.104557
Gasque P, Bandjee MC, Reyes MM, Viasus D. Chikungunya pathogenesis: From the clinics to the bench. J Infect Dis. 2016;214(Suppl.5):S446-S8. https://doi.org/10.1093/infdis/jiw362
Flórez-Lozano K, Navarro-Lechuga E, Llinas-Solano H, Tuesca-Molina R, Sisa-Camargo A, Mercado-Reyes M, et al. Spatial distribution of the relative risk of Zika virus disease in Colombia during the 2015-2016 epidemic from a Bayesian approach. Int J Gynaecol Obstet. 2020;148(Suppl.2):55-60. https://doi.org/10.1002/ijgo.13048
Pollett S, Fauver JR, Maljkovic Berry I, Meléndrez M, Morrison A, Gillis LD, et al. Genomic epidemiology as a public health tool to combat mosquito-borne virus outbreaks. J Infect Dis. 2020;221(Suppl.3):S308-18. https://doi.org/10.1093/infdis/jiz302
Laiton-Donato K, Usme-Ciro JA, Rico A, Pardo L, Martínez C, Salas D, et al. Análisis filogenético del virus del chikungunya en Colombia: evidencia de selección purificadora en el gen E1. Biomédica. 2016;36:25-34. https://doi.org/10.7705/biomedica.v36i0.2990
Laiton-Donato K, Álvarez DA, Peláez-Carvajal D, Mercado M, Ajami NJ, Bosch I, et al. Molecular characterization of dengue virus reveals regional diversification of serotype 2 in Colombia. Virol J. 2019;16:62. https://doi.org/10.1186/s12985-019-1170-4
Black A, Moncla LH, Laiton-Donato K, Potter B, Pardo L, Rico A, et al. Genomic epidemiology supports multiple introductions and cryptic transmission of Zika virus in Colombia. BMC Infect Dis. 2019;19:963. https://doi.org/10.1186/s12879-019-4566-2
Laiton-Donato K, Villabona-Arenas CJ, Usme-Ciro JA, Franco-Muñoz C, Álvarez-Díaz DA, Villabona-Arenas LS, et al. Genomic epidemiology of Severe Acute Respiratory Syndrome Coronavirus 2, Colombia. Emerg Infect Dis. 2020;26. https://doi.org/10.1101/2020.06.26.20135715
Ramírez JD, Muñoz M, Hernández C, Flórez C, Gómez S, Rico A, et al. Genetic diversity among SARS-CoV2 strains in South America may impact performance of molecular detection. Pathogens. 2020;9:580. https://doi.org/10.3390/pathogens9070580
Resende PC, Delatorre E, Gräf T, Mir D, Motta FdC, Appolinario LR, et al. Genomic surveillance of SARS-CoV-2 reveals community transmission of a major lineage during the early pandemic phase in Brazil. bioRxiv. 2020. https://doi.org/10.1101/2020.06.17.158006
Zhang L, Jackson CB, Mou H, Ojha A, Rangarajan ES, Izard T, et al. The D614G mutation in the SARS-CoV-2 spike protein reduces S1 shedding and increases infectivity. bioRxiv. 2020. https://doi.org/10.1101/2020.06.12.148726
Korber B, Fischer WM, Gnanakaran S, Yoon H, Theiler J, Abfalterer W, et al. Tracking changes in SARS-CoV-2 Spike: Evidence that D614G Increases Infectivity of the COVID-19 Virus. Cell. 2020;182:812-27. https://doi.org/10.1016/j.cell.2020.06.043
Kim SJ, Nguyen VG, Park YH, Park BK, Chung HC. A novel synonymous mutation of SARSCoV-2: Is this possible to affect their antigenicity and immunogenicity? Vaccines (Basel).2020;8:220. https://doi.org/10.3390/vaccines8020220
Jesus JG, Sacchi C, Candido DDS, Claro IM, Sales FCS, Manuli ER, et al. Importation and early local transmission of COVID-19 in Brazil, 2020. Rev Inst Med Trop Sao Paulo. 2020;62:e30. https://doi.org/10.1590/s1678-9946202062030
Candido DS, Claro IM, de Jesus JG, Souza WM, Moreira FRR, Dellicour S, et al. Evolution and epidemic spread of SARS-CoV-2 in Brazil. Science. 2020;369:1255-60. https://doi.org/10.1126/science.abd2161
Xavier J, Giovanetti M, Adelino T, Fonseca V, Barbosa da Costa AV, Ribeiro AA, et al. The ongoing COVID-19 epidemic in Minas Gerais, Brazil: Insights from epidemiological data and SARS-CoV-2 whole genome sequencing. Emerg Microbes Infect. 2020;9:1824-34. https://doi.org/10.1080/22221751.2020.1803146
López-Álvarez D, Parra B, Cuéllar WJ. Genome sequence of SARS-CoV-2 isolate Cali-01, from Colombia, obtained using Oxford Nanopore MinION Sequencing. Microbiol Resour Announc. 2020;9:e00573-20. https://doi.org/10.1128/MRA.00573-20
Paniz-Mondolfi A, Muñoz M, Flórez C, Gómez S, Rico A, Pardo L, et al. SARS-CoV-2 spreadacross the Colombian-Venezuelan border. medRxiv. 2020. https://doi.org/10.1101/2020.07.09.20149856
Castillo AE, Parra B, Tapia P, Acevedo A, Lagos J, Andrade W, et al. Phylogenetic analysis of the first four SARS-CoV-2 cases in Chile. J Med Virol. 2020;92:1562-6. https://doi.org/10.1002/jmv.25797
Márquez S, Prado-Vivar B, Guadalupe JJ, Gutiérrez Granja B, Jibaja M, Tobar M, et al. Genome sequencing of the first SARS-CoV-2 reported from patients with COVID-19 in Ecuador. medRxiv. 2020. https://doi.org/10.1101/2020.06.11.20128330
Garcés-Ayala F, Araiza-Rodríguez A, Mendieta-Condado E, Rodríguez-Maldonado AP,Wong-Arambula C, Landa-Flores M, et al. Full genome sequence of the first SARS-CoV-2 detected in México. Arch Virol. 2020;165:2095-8. https://doi.org/10.1007/s00705-020-04695-3
Franco D, González C, Abrego LE, Carrera JP, Díaz Y, Caisedo Y, et al. Early transmission dynamics, spread, and genomic characterization of SARS-CoV-2 in Panama. medRxiv. 2020. https://doi.org/10.1101/2020.07.31.20160929
Padilla-Rojas C, Lope-Pari P, Vega-Chozo K, Balbuena-Torres J, Cáceres-Rey O, Bailón-Calderón H, et al. Near-complete genome sequence of a 2019 novel coronavirus (SARSCoV-2) strain causing a COVID-19 case in Perú. Microbiol Resour Announc. 2020;9:e00303-20. https://doi.org/10.1128/MRA.00303-20
Padilla-Rojas C, Vega-Chozo K, Galarza-Pérez M, Calderón HB, Lope-Pari P, Balbuena-Torres J, et al. Genomic analysis reveals local transmission of SARS-CoV-2 in early pandemic phase in Perú. bioRxiv. 2020. https://doi.org/10.1101/2020.09.05.284604
Juscamayta-López E, Tarazona D, Valdivia F, Rojas N, Carhuaricra D, Maturrano L, et al. Phylogenomic reveals multiple introductions and early spread of SARS-CoV-2 into Perú. bioRxiv. 2020. https://doi.org/10.1101/2020.09.14.296814
Poterico JA, Mestanza O. Genetic variants and source of introduction of SARS-CoV-2 in South America. J Med Virol. 2020;92:2139-45. https://doi.org/10.1002/jmv.26001
Salazar C, Díaz-Viraqué F, Pereira-Gómez M, Ferrés I, Moreno P, Moratorio G, et al. Multiple introductions, regional spread and local differentiation during the first week of COVID-19 epidemic in Montevideo, Uruguay. bioRxiv. 2020. https://doi.org/10.1101/2020.05.09.086223
Díaz FJ, Aguilar-Jiménez W, Flórez-Álvarez L, Valencia G, Laiton-Donato K, Franco-Muñoz, et al. Aislamiento y caracterización de una cepa temprana de la epidemia de SARS-CoV-2 de 2020 en Medellín, Colombia. Biomédica. 2020;40(Supl.2):148-58. https://doi.org/10.7705/biomedica.5834
Algunos artículos similares:
- Yesika del Carmen Rojas, Helena Brochero, Hallazgo de Aedes aegypti (Linnaeus 1762), en el casco urbano del corregimiento de La Pedrera, Amazonas, Colombia , Biomédica: Vol. 28 Núm. 4 (2008)
- Luz Elena Velásquez, Catalina Gómez, Erika Valencia, Laura Salazar, Eudoro Casas, Estudio de foco de paragonimosis en Fuente Clara, Robledo, área periurbana de Medellín, Antioquia , Biomédica: Vol. 28 Núm. 3 (2008)
- José Alejandro Martínez-Ibarra, Jorge Alejandro Martínez-Grant, Miguel Roberto Verdugo-Cervantes, Rafael Bustos-Saldaña, Benjamín Nogueda-Torres, Vigilancia de la presencia de triatominos mediante gallineros en el sur de Jalisco, México , Biomédica: Vol. 30 Núm. 1 (2010)
- Sandra Milena Arias, Lina Marcela Salazar, Eudoro Casas, Alexandra Henao, Luz Elena Velásquez, Paragonimus sp. en cangrejos y sensibilización de la comunidad educativa hacia los ecosistemas acuáticos de La Miel y La Clara, Caldas, Antioquia , Biomédica: Vol. 31 Núm. 2 (2011)
- Marylin Hidalgo, Claudia Santos, Carolina Duarte, Elizabeth Castañeda, Clara Inés Agudelo, Incremento de la resistencia a eritromicina de Streptococcus pneumoniae, Colombia, 1994-2008 , Biomédica: Vol. 31 Núm. 1 (2011)
- Myrtha Arango, Elizabeth Castañeda, Clara Inés Agudelo, Catalina De Bedout, Carlos Andrés Agudelo, Angela Tobón, Melva Linares, Yorlady Valencia, Ángela Restrepo, The Colombian Histoplasmosis Study Group, Histoplasmosis en Colombia: resultados de la encuesta nacional, 1992-2008 , Biomédica: Vol. 31 Núm. 3 (2011)
- Jaiberth Cardona-Arias, Luz Peláez-Vanegas, Juan López-Saldarriaga, Marcela Duque-Molina, Oscar Leal-Álvarez, Calidad de vida relacionada con la salud en adultos con VIH/sida, Medellín, Colombia, 2009 , Biomédica: Vol. 31 Núm. 4 (2011)
- Pablo Chaparro, Edison Soto, Julio Padilla, Daniel Vargas, Estimación del subregistro de casos de paludismo en diez municipios de la costa del Pacífico nariñense durante 2009 , Biomédica: Vol. 32 (2012): Suplemento 1, Malaria
- Jorge Andrés Cuellar, Alejandro Hernández, Enrique Villegas, Jorge Enrique Gómez, Eficiencia de cultivo in vitro de Toxoplasma gondii en las líneas celulares THP1 y Vero , Biomédica: Vol. 32 Núm. 3 (2012)
- Yiby Forero, Gina E. Morales, Edgar Benítez, Comparación de dos metodologías utilizadas para la determinación del síndrome metabólico en población adulta , Biomédica: Vol. 33 Núm. 2 (2013)
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |

























