Clasificación de la expresión del receptor 2 del factor de crecimiento epidérmico humano en tejido mamario canceroso mediante inteligencia artificial
Resumen
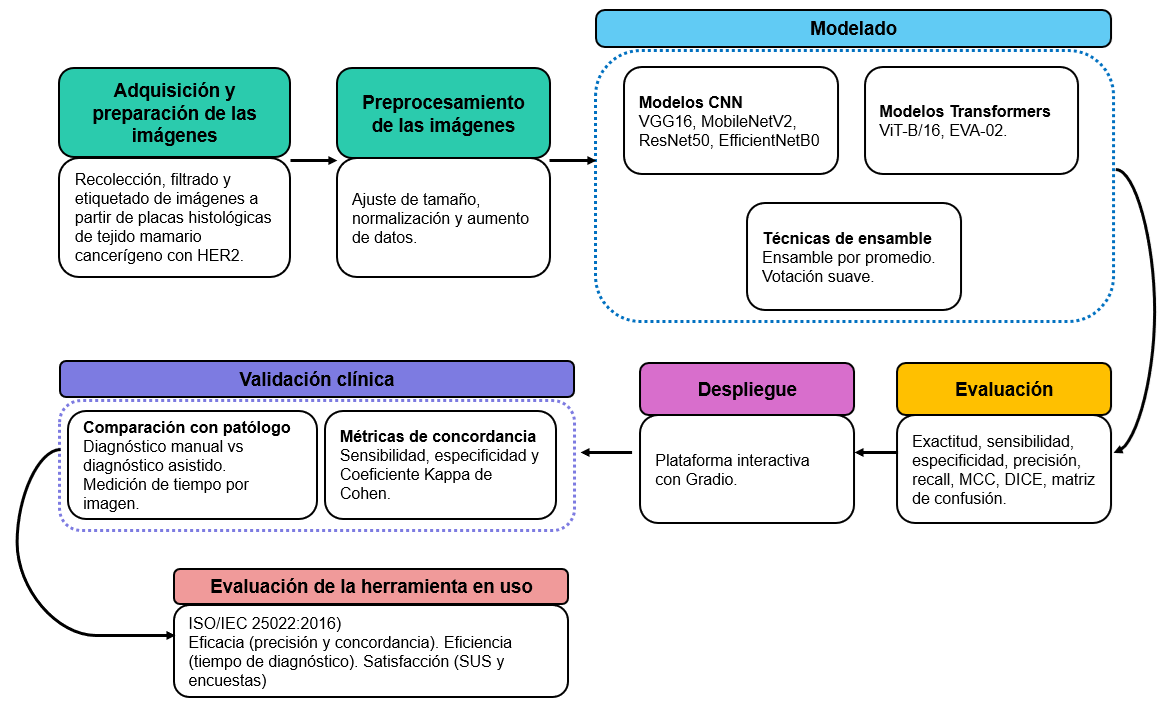
Introducción. El análisis histológico y molecular del tejido mamario es clave para el diagnóstico, el pronóstico y el tratamiento del cáncer de mama. Entre los biomarcadores evaluados, se destacan los receptores de progesterona, los de estrógeno y el receptor 2 del factor de crecimiento epidérmico humano (HER2). La sobreexpresión de HER2 indica un subtipo agresivo de cáncer de mama, aunque permite el uso de terapias dirigidas que mejoran la tasa de supervivencia. No obstante, su evaluación enfrenta desafíos, desde la calidad de las muestras hasta la variabilidad en la interpretación. El College of American Pathologists clasifica la sobreexpresión de HER2 en cuatro categorías, pero la variabilidad en la expresión cercana al 10 % puede generar confusión.
Objetivo. Presentar una técnica basada en la inteligencia artificial para clasificar células con sobreexpresión de HER2 en las placas histológicas.
Materiales y métodos. Se aplicó la metodología Cross-Industry Standard Process for Data Mining (CRISP-DM) en muestras de 89 pacientes de la Unidad de Diagnóstico en Patología, abarcando los cuatro niveles de HER2. Se utilizaron redes neuronales y modelos de Vision Transformer (ViT) afinados mediante transferencia de aprendizaje. Además, se evaluó la facilidad de uso y, finalmente, la eficiencia del software presentado.
Resultados. Con el modelo ViT-B/16, se obtuvo una exactitud del 90,65 % en la clasificación, mientras que la herramienta evaluada generó un grado aceptable de satisfacción con su aplicación clínica.
Conclusión. La inteligencia artificial demostró gran precisión y concordancia en la clasificación del HER2, redujo la variabilidad diagnóstica y mejoró la objetividad, aunque aún se requiere optimizar la eficiencia del procesamiento.
Descargas
Referencias bibliográficas
American Cancer Society. What is cancer | Cancer basics. Fecha de consulta: 22 de diciembre de 2024. Disponible en: https://www.cancer.org/cancer/understanding-cancer/what-is-cancer.html
Bórquez S, Pezoa R, Salinas L, Torres CE. Uncertainty estimation in the classification of histopathological images with HER2 overexpression using Monte Carlo Dropout. Biomed Signal Process Control. 2023;85:104864. https://doi.org/10.1016/j.bspc.2023.104864
Swain SM, Shastry M, Hamilton E. Targeting HER2-positive breast cancer: Advances and future directions. Nat Rev Drug Discov. 2023;22:101‑26. https://doi.org/10.1038/s41573-022-00579-0
American Cancer Society. Breast cancer HER2 status | What is HER2 status? Fecha de consulta: 22 de diciembre de 2024. Disponible en: https://www.cancer.org/cancer/types/breast-cancer/understanding-a-breast-cancer-diagnosis/breast-cancer-her2-status.html
American Society of Clinical Oncology. Breast cancer. Fecha de consulta: 22 de diciembre de 2024. Disponible en: https://society.asco.org/practice-patients/guidelines/breast-cancer
International Agency for Research on Cancer. Cancer today. Fecha de consulta: 22 de diciembre de 2024. Disponible en: https://gco.iarc.who.int/today/
Departamento Administrativo Nacional de Estadística. Defunciones no fetales 2020. Fecha de consulta: 22 de diciembre de 2024. Disponible en: https://www.dane.gov.co/index.php/estadisticas-por-tema/salud/nacimientos-y-defunciones/defunciones-no-fetales/defuncionesno-fetales-2020
Zheng Y, Liang H, Zhao S. LMBNet: Lightweight multiple branch network for recognition of HER2 expression levels. Proc Comput Sci. 2023;222:197‑206. https://doi.org/10.1016/j.procs.2023.08.157
Córdova C, Muñoz R, Olivares R, Minonzio JG, Lozano C, González P, et al. HER2 classification in breast cancer cells: A new explainable machine learning application for immunohistochemistry. Oncol Lett. 2023;25:44. https://doi.org/10.3892/ol.2022.13630
Wang X, Shao C, Liu W, Liang H, Li N. HER2‑ResNet: A HER2 classification method based on deep residual network. Technol Health Care. 2022;30(Supl.1):215‑24. https://doi.org/10.3233/THC-228020
Mirimoghaddam MM, Majidpour J, Pashaei F, Arabalibeik H, Samizadeh E, Roshan NM, et al. HER2GAN: Overcome the scarcity of HER2 breast cancer dataset based on transfer learning and GAN Model. Clin Breast Cancer. 2024;24:53‑64. https://doi.org/10.1016/j.clbc.2023.09.014
Selcuk SY, Yang X, Bai B, Zhang Y, Li Y, Aydin M, et al. Automated HER2 scoring in breast cancer images using deep learning and pyramid sampling. BME Front. 2024;5:00‑48. https://doi.org/10.34133/bmef.0048
Chauhan R, Ghanshala KK, Joshi RC. Convolutional Neural Network (CNN) for image detection and recognition. In: First International Conference on Secure Cyber Computing and Communication (ICSCCC); 2018. Jalandhar, India: IEEE; 2018. p. 278‑82. https://doi.org/10.1109/ICSCCC.2018.8703316
Vaswani A, Shazeer N, Parmar N, Uszkoreit J, Jones L, Gómez AN, et al. Attention is all you need. Preprint. arXiv; 2023. arXiv:1706.03762. https://doi.org/10.48550/arXiv.1706.03762
Dosovitskiy A, Beyer L, Kolesnikov A, Weissenborn D, Zhai X, Unterthiner T, et al. An image is worth 16 × 16 words: Transformers for image recognition at scale. Preprint. arXiv; 2021. arXiv:2010.11929. https://doi.org/10.48550/arXiv.2010.11929
Liu Z, Lin Y, Cao Y, Hu H, Wei Y, Zhang Z, et al. Swin transformer: Hierarchical vision transformer using shifted windows. Preprint. arXiv; 2021. arXiv:2103.14030. https://doi.org/10.48550/arXiv.2103.14030
Khan S, Naseer M, Hayat M, Zamir SW, Khan FS, Shah M. Transformers in vision: A survey. ACM Comput Surv. 2022;54(10s):1‑41. https://doi.org/10.1145/3505244
Chollet F. Deep learning with Python. Second edition. New York, NY: Simon and Schuster; 2021. p. 1‑502.
Theckedath D, Sedamkar RR. Detecting affect states using VGG16, ResNet50 and SE‑ResNet50 networks. SN Comput Sci. 2020;1:79. https://doi.org/10.1007/s42979-020-0114-9
Özaltın Ö, Yeniay Ö. Detection of monkeypox disease from skin lesion images using mobilenetv2 architecture. Communications Faculty of Sciences University of Ankara Series A1 Mathematics and Statistics. 2023;72:482‑99. https://doi.org/10.31801/cfsuasmas.1202806
Tan M, Le QV. EfficientNet: Rethinking model scaling for convolutional neural networks. Preprint. arXiv; 2020. arXiv:1905.11946. https://doi.org/10.48550/arXiv.1905.11946
Fang Y, Sun Q, Wang X, Huang T, Wang X, Cao Y. EVA-02: A visual representation for Neon Genesis. Image Vis Comput. 2024;149:105‑71. https://doi.org/10.1016/j.imavis.2024.105171
Stanford Vision Lab; Princeton University. ImageNet. Fecha de consulta: 13 de febrero de 2025. Disponible en: https://www.image-net.org/
Shaga Devan K, Kestler HA, Read C, Walther P. Weighted average ensemble-based semantic segmentation in biological electron microscopy images. Histochem Cell Biol. 2022;158:447‑62. https://doi.org/10.1007/s00418-022-02148-3
Zhou ZH. Ensemble methods: Foundations and algorithms. First edition. Boca Ratón, FL: Chapman & Hall/CRC; 2012. p. 1‑236.
Gradio. Gradio App. Fecha de consulta: 12 de febrero de 2025. Disponible en: https://www.gradio.app/
International Organization for Standardization (ISO). ISO/IEC 25022:2016 — Systems and software engineering — Systems and software quality requirements and evaluation (SQuaRE) - Measurement of quality in use. Fecha de consulta: 12 de febrero de 2025. Disponible en: https://www.iso.org/standard/35746.html
Brooke J. SUS - A quick and dirty usability scale. Fecha de consulta: 12 de febrero de 2025. Disponible en: https://digital.ahrq.gov/sites/default/files/docs/survey/systemusabilityscale%2528sus%2529_comp%255B1%255D.pdf
Algunos artículos similares:
- Edwin Abraham Medina, Adenoma del oído medio , Biomédica: Vol. 29 Núm. 3 (2009)
- Aura Caterine Rengifo, Orlando Torres-Fernández, Disminución del número de neuronas que expresan GABA en la corteza cerebral de ratones infectados con rabia , Biomédica: Vol. 27 Núm. 4 (2007)
- Oscar F. Herrán, María F. Ardila, Martha P. Rojas, Gustavo A. Hernández, Diseño de cuestionarios de frecuencia de consumo para estudiar la relación dieta-cáncer en Colombia , Biomédica: Vol. 30 Núm. 1 (2010)
- Nina Paola Lamprea, Lina María Ortega, Gerardo Santamaría, Ladys Sarmiento, Orlando Torres-Fernández, Elaboración y evaluación de un antisuero para la detección inmunohistoquímica del virus de la rabia en tejido cerebral fijado en aldehídos , Biomédica: Vol. 30 Núm. 1 (2010)
- Juan Carlos Cataño, Síndrome miasténico de Eaton-Lambert , Biomédica: Vol. 30 Núm. 3 (2010)
- Juan Carlos Herrera, Luis Fernando Isaza, José Luis Ramírez, Gonzalo Vásquez, Carlos Mario Muñetón, Detección de aneuploidías del cromosoma 17 y deleción del gen TP53 en una amplia variedad de tumores sólidos mediante hibridación in situ fluorescente bicolor , Biomédica: Vol. 30 Núm. 3 (2010)
- Yaliana Tafurt-Cardona, Leidy D. Jaramillo-Ruiz, Wilson Muñoz-Ordóñez, Sulma L. Muñoz-Benítez, Carlos H. Sierra-Torres, Mayor frecuencia de aberraciones cromosómicas en linfocitos expuestos o no a mitomicina C, de mujeres posmenopáusicas obesas en comparación con mujeres no obesas del departamento del Cauca, Colombia , Biomédica: Vol. 32 Núm. 3 (2012)
- Ricardo Cendales, Constanza Pardo, Claudia Uribe, Guillermo López, María Clara Yépez, Luis Eduardo Bravo, Calidad de los datos en los registros de cáncer de base de población en Colombia , Biomédica: Vol. 32 Núm. 4 (2012)
- Sonia Isabel Cuervo, Ricardo Sánchez, Julio César Gómez-Rincón, Cielo Almenares, Juan Pablo Osorio, María José Vargas, Comportamiento de casos de Klebsiella pneumoniae productora de carbapenemasas en pacientes con cáncer de un hospital de tercer nivel de Bogotá, D.C. , Biomédica: Vol. 34 (2014): Abril, Suplemento 1, Resistencia bacteriana
- Jeison Monroy-Gómez, Orlando Torres-Fernández, Distribución de calbindina y parvoalbúmina y efecto del virus de la rabia sobre su expresión en la médula espinal de ratones , Biomédica: Vol. 33 Núm. 4 (2013)
Derechos de autor 2025 Biomédica

Esta obra está bajo una licencia internacional Creative Commons Atribución 4.0.
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |

























