Correlación entre el número de variantes de falsos positivos y la calidad de los resultados en la secuenciación con Ion Torrent PGM™ para seleccionar genes BRCA
Resumen
Introducción. La secuenciación de nueva generación es un método rentable y rápido para el estudio de los genes, pero su protocolo entraña desafíos.
Objetivo. Investigar diferentes ajustes del protocolo de selección de los genes BRCA mediante secuenciación de Ion Torrent PGM™ y correlacionar los resultados con el número de variantes de falso positivo.
Materiales y métodos. El proceso de preparación de la biblioteca, el número de falsos positivos InDels, la concentración de la biblioteca, el número de ciclos en el paso de amplificación de objetivos, la pureza del ácido nucleico, la entrada y el número de muestras por chip del Ion-314 se analizaron en asociación con los resultados obtenidos por secuenciación de nueva generación secuenciación de nueva generación.
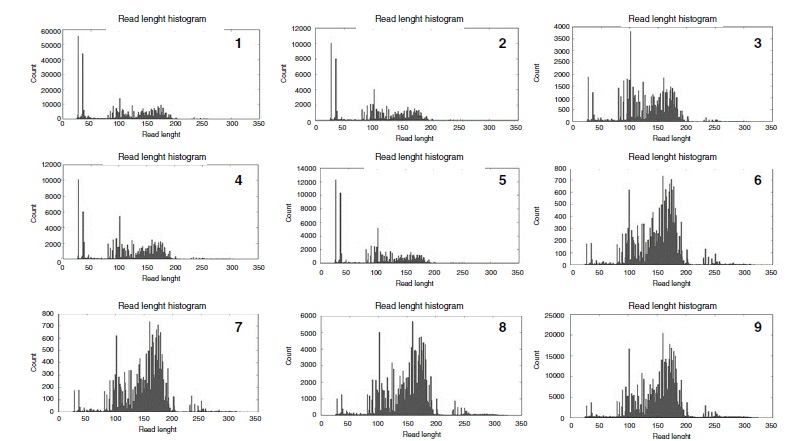
Resultados. Se hicieron 51 reacciones y nueve ajustes de los protocolos, y se observaron ocho falsos positivos InDels en las regiones de homopolímeros. No se observó ninguna variante de polimorfismo de nucleótido simple falso positivo. En 67,5 % de los casos, las variables de protocolo en su conjunto se asociaron con la calidad de los resultados obtenidos (p<0,05). El número de falsos positivos InDels disminuyó al aumentar la calidad de los resultados.
Conclusiones. El panel comunitario Ion AmpliSeq BRCA1/BRCA2 tuvo un mejor rendimiento, con cuatro muestras por chip Ion-314 en lugar de ocho, y el número de ciclos en el paso de amplificación, incluso con ADN de alta calidad, fue mejor con 23. Se observaron mejores resultados con el proceso de ecualización manual y sin el uso del kit Ion Library Equalizer. Estos ajustes proporcionaron una mayor cobertura de las variantes y menos artefactos. Los laboratorios deben realizar la validación interna porque las variantes de falsos positivos InDel pueden variar según la calidad de los resultados. La secuenciación de próxima generación debe validarse con Sanger.
Descargas
Referencias bibliográficas
Niell BL, Rennert G, Bonner JD, Almog R, Tomsho LP, Gruber SB. BRCA1 and BRCA2 founder mutations and the risk of colorectal cancer. J Natl Cancer Inst. 2004;96:15-21. https://doi.org/10.1093/jnci/djh008
Garber JE, Syngal S. One less thing to worry about: The shrinking spectrum of tumors in BRCA founder mutation carriers. J Natl Cancer Inst. 2004;96:2-310. https://doi.org/1093/jnci/djh021
Wallace AJ. New challenges for BRCA testing: A view from the diagnostic laboratory. Eur J Hum Genet. 2016;24(Suppl.1):S10-18. https://doi.org/10.1038/ejhg.2016.94
Loeffelholz M, Fofanov Y. The main challenges that remain in applying high-throughput sequencing to clinical diagnostics. Expert Rev Mol Diagn. 2015;15:1405-8. https://doi.org/10.1586/14737159.2015.1088385
Germani A, Libi F, Maggi S, Stanzani G, Lombardi A, Pellegrini P, et al. Rapid detection of copy number variations and point mutations in BRCA1/2 genes using a single workflow by ion semiconductor sequencing pipeline. Oncotarget. 2018;9:33648-55. https://doi.org/10.18632/oncotarget.26000
Zanella I, Merola F, Biasiotto G, Archetti S, Spinelli E, Di Lorenzo D. Evaluation of the Ion Torrent PGM sequencing workflow for the routine rapid detection of BRCA1 and BRCA2 germline mutations. Exp Mol Pathol. 2017;102:314-20. https://doi.org/10.1016/j.yexmp.2017.03.001
Oosterwijk JC, de Vries J, Mourits MJ, de Bock GH. Genetic testing and familial implications in breast-ovarian cancer families. Maturitas. 2014;78:252-7. https://doi.org/10.1016/j.maturitas.2014.05.002
Claus EB, Schildkraut JM, Thompson D, Risch NJ.The genetic attributable risk of breast and ovarian cancer. Cancer. 1996;77:2318-24. https://doi.org/10.1002/(SICI)1097-0142(19960601)77:11<2318::AID-CNCR21>3.0.CO;2-Z
Lih CJ, Harrington RD, Sims DJ, Harper KN, Bouk CH, Datta V, et al. Analytical validation of the next-generation sequencing assay for a nationwide signal-finding clinical trial: Molecular analysis for therapy choice clinical trial. J Mol Diagn. 2017;19:313-27. https://doi.org/10.1016/j.jmoldx.2016.10.007
Maistro S, Teixeira N, Encinas G, Katayama ML, Niewiadonski VD, Cabral LG, et al. Germline mutations in BRCA1 and BRCA2 in epithelial ovarian cancer patients in Brazil. BMC Cancer. 2016;16:934. https://doi.org/10.1186/s12885-016-2966-x
Bragg LM, Stone G, Butler MK, Hugenholtz P, Tyson GW. Shining a light on dark sequencing: Characterising errors in Ion Torrent PGM data. PLoS Comput Biol. 2013;9:e1003031. https://doi.org/10.1371/journal.pcbi.1003031
Kang HP, Maguire JR, Chu CS, Haque IS, Lai H, Mar-Heyming R, et al. Design and validation of a next generation sequencing assay for hereditary BRCA1 and BRCA2 mutation testing. Peer J. 2016;4:e2162. https://doi.org/10.7717/peerj.2162
Park J, Jang W, Chae H, Kim Y, Chi HY, Kim M. Comparison of targeted next-generation and Sanger sequencing for the BRCA1 and BRCA2 mutation screening. Ann Lab Med. 2016;36:197-201. https://doi.org/201603197
Mehta A, Vasudevan S, Sharma SK, Kumar D, Panigrahi M, Suryavanshi M, et al. Germline BRCA1 and BRCA2 deleterious mutations and variants of unknown clinical significance associated with breast/ovarian cancer: A report from North India. Cancer Manag Res. 2018;10:6505-16. https://doi.org/10.2147/CMAR.S186563
Rehm HL, Bale SJ, Bayrak-Toydemir P, Berg JS, Brown KK, Deignan JL, et al. ACMG clinical laboratory standards for next-generation sequencing. Genet Med. 2013;15:733-47. https://doi.org/10.1038/gim.2013.92
Trujillano D, Weiss ME, Schneider J, Koster J, Papachristos EB, Saviouk V, et al. Nextgeneration sequencing of the BRCA1 and BRCA2 genes for the genetic diagnostics of hereditary breast and/or ovarian cancer. J Mol Diagn. 2015;17:162-70. https://doi.org/10.1016/j.jmoldx.2014.11.004
Sanger F, Nicklen S, Coulson AR. DNA sequencing with chain-terminating inhibitors. Proc Natl Acad Sci USA. 1977;74:5463-7. https://doi.org/10.1073/pnas.74.12.5463
Vendrell JA, Vilquin P, Larrieux M, van Goethem C, Solassol J. Benchmarking of ampliconbased next-generation sequencing panels combined with bioinformatics solutions for germline BRCA1 and BRCA2 alteration detection. J Mol Diagn. 2018;20:754-64. https://doi.org/S1525-1578(18)30072-2 19
Jennings LJ, Arcila ME, Corless C, Kamel-Reid S, Lubin IM, Pfeifer J, et al. Guidelines for validation of next-generation sequencing-based oncology panels: A joint consensus recommendation of the Association for Molecular Pathology and College of American Pathologists. J Mol Diagn. 2017;19:341-65. https://doi.org/S1525-1578(17)30025-9
Beck TF, Mullikin JC, Program NCS, Biesecker LG. Systematic evaluation of Sanger validation of next-generation sequencing variants. Clin Chem. 2016;62:647-54. https://doi.org/10.1373/clinchem.2015.249623
Buzolin AL, Moreira CM, Sacramento PR, Oku AY, Fornari A, Antonio DSM, et al. Development and validation of a variant detection workflow for BRCA1 and BRCA2 genes and its clinical application based on the Ion Torrent technology. Hum Genomics. 2017;11:14. https://doi.org/10.1186/s40246-017-0110-x
Harismendy O, Ng PC, Strausberg RL, Wang X, Stockwell TB, Beeson KY, et al. Evaluation of next generation sequencing platforms for population targeted sequencing studies. Genome Biol. 2009;10:R32. https://doi.org/10.1186/gb-2009-10-3-r32
Strom CM, Rivera S, Elzinga C, Angeloni T, Rosenthal SH, Goos-Root D, et al. Development and validation of a next-generation sequencing assay for BRCA1 and BRCA2 variants for the clinical laboratory. PLoS ONE. 2015;10:e0136419. https://doi.org/10.1371/journal.pone.0136419
Bijwaard K, Dickey JS, Kelm K, Tezak Z. The first FDA marketing authorizations of next generation sequencing technology and tests: Challenges, solutions and impact for future assays. Expert Rev Mol Diagn. 2015;15:33-40. https://doi.org/10.1586/14737159.2015.979795
Gargis AS, Kalman L, Berry MW, Bick DP, Dimmock DP, Hambuch T, et al. Assuring the quality of next-generation sequencing in clinical laboratory practice. Nat Biotechnol. 2012;30:1033-6. https://doi.org/10.1038/nbt.2403
Algunos artículos similares:
- Brian Alejandro Suárez, Claudia Liliana Cuervo, Concepción Judith Puerta, La región intergénica del gen H2A apoya las subpoblaciones KP1(-) y KP1(+) de Trypanosoma rangeli , Biomédica: Vol. 27 Núm. 3 (2007)
- Patricia Escandón, Popchai Ngamskulrungroj, Wieland Meyer, Elizabeth Castañeda, Determinación in vitro de la pareja sexual en aislamientos del complejo Cryptococcus neoformans , Biomédica: Vol. 27 Núm. 2 (2007)
- Andrea Gómez, Gustavo Salguero, Herbert García, Fabio Aristizábal, Oscar Gutiérrez, Luis Alberto Angel, Jorge Padrón, Carlos Martínez, Humberto Martínez, Omar Malaver, Rosa Barvo, Alejandro Giraldo, Detección de mutaciones de los genes hMLH1 y hMSH2 del sistema de reparación de malos apareamientos del ADN en familias colombianas sospechosas de cancer colorrectal no polipósico hereditario (síndrome de Lynch). , Biomédica: Vol. 25 Núm. 3 (2005)
- Diana León-Luna , Alexander Fajardo-Loyola , José Yareta-Yareta , Antonio Burgos-Espejo , Carlos Peralta-Siesquen , Marco Galarza-Pérez , Pool Marcos-Carbajal, Caracterización molecular de enterobacterias multirresistentes en dos departamentos de la selva peruana , Biomédica: Vol. 41 Núm. Sp. 2 (2021): Octubre, Infecciones bacterianas y virales
- Jimena Jaramillo, Juan M. Solano, Alejandra Aristizábal, Juliana Martínez , Análisis de mutaciones en los genes SOD1 y C9orf72 en pacientes con esclerosis lateral amiotrófica, Antioquia, Colombia , Biomédica: Vol. 42 Núm. 4 (2022)
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |

























